Revista Veterinaria. 2026; 37(1)
https://doi.org/10.30972/vet.3719046
Artículo Original




1Facultad de Ciencias Agropecuarias, Universidad Católica de Córdoba (UCC).
2Unidad Ejecutora IRNASUS CONICET-UCC. Av. Armada Argentina 3555, Córdoba X5016DHK, Argentina.
 nlitterio@ucc.edu.ar
nlitterio@ucc.edu.ar
Recibido: 11 julio 2025 / Aceptado: 16 octubre 2025
Resumen
La diarrea posdestete (DPD) es un importante problema sanitario y económico en la producción porcina, donde Escherichia coli enterotoxigénica (ETEC) constituye uno de los principales agentes causales, provocando diarrea y retraso en el crecimiento, lo que conlleva un mayor uso de antimicrobianos y, en consecuencia, un incremento del riesgo de resistencia bacteriana. El objetivo de este estudio fue aislar cepas de E. coli a partir de muestras fecales de lechones con DPD en granjas de la provincia de Córdoba, Argentina, describir su perfil de resistencia a antimicrobianos de importancia crítica en salud pública y/o animal, y realizar su caracterización genotípica. Se recolectaron 69 muestras de hisopado rectal en seis establecimientos, con una tasa de aislamiento de E. coli del 97%. Se observó un perfil de resistencia preocupante, con altos niveles frente a betalactámicos (98,5%), fenicoles (88%), tetraciclinas (86,6%) y aminoglucósidos (34,3%). Además, 62 cepas (92,5%) fueron clasificadas como multirresistentes. De los 67 aislamientos obtenidos, el 70% correspondió a cepas ETEC, con alta prevalencia de los genes estII (74,5%) y estI (63,8%), asociados a la producción de toxinas. También se detectaron genes de adhesión como fedA (21,3%), faeG (14,9%), aidA(25,5%) y astA (14,9%). Estos resultados evidencian la fuerte presión de selección ejercida sobre las poblaciones bacterianas en los sistemas productivos, favoreciendo la persistencia y diseminación de cepas multirresistentes, y subrayan la necesidad de implementar medidas de control más estrictas para reducir su propagación en la producción porcina, con implicancias directas para la salud pública y bajo el enfoque de Una Salud.
Palabras clave: Colibacilosis,ETEC, resistencia antimicrobiana, diarrea posdestete, vigilancia epidemiológica, Una Salud.
Abstract:Abstract. Post-weaning diarrhea (PWD) is a major health and economic issue problem in swine production, where enterotoxigenic Escherichia coli (ETEC) is one of the main causative agents. It leads to diarrhea and growth retardation, which resulting in increased antimicrobial use and, consequently, a higher risk of bacterial resistance. This study aimed to isolate E. coli strains from fecal samples of piglets with PWD on farms in Córdoba province, Argentina, to describe their antimicrobial resistance profiles and perform genotypic characterization. A total of 69 rectal swabs were collected from six farms; E. coli was isolated in 97% of the samples. A concerning resistance profile was observed, with high levels against β-lactams (98.5%), phenicols (88%), tetracyclines (86.6%), and aminoglycosides (34.3%). Moreover, 62 strains (92.5%) were classified as multidrug-resistant. Among the 67 isolates obtained, 70% corresponded to ETEC strains, showing a high prevalence of the toxin-associated genes estII (74.5%) and estI (63.8%). Adhesion genes were also detected, including fedA (21.3%), faeG (14.9%), aidA(25.5%), and astA (14.9%). These findings highlight the strong selective pressure exerted on bacterial populations in production systems, favoring the persistence and dissemination of multidrug-resistant strains. They also emphasize the need to implement stricter control measures to reduce their spread in swine production, with direct implications for public health under the One Health approach.
Key words: colibacillosis, ETEC, antimicrobial resistance, post-weaning diarrhea, epidemiological surveillance, One Health.
La diarrea posdestete (DPD) es un problema frecuente en explotaciones porcinas de todo el mundo y representa una enfermedad de gran impacto económico, especialmente en granjas de confinamiento. Afecta a los animales durante las dos primeras semanas tras el destete, ocasionando retraso en el crecimiento e incluso la muerte en algunos casos. Su origen es multifactorial e incluye factores ambientales, sociales y nutricionales: el reagrupamiento, el hacinamiento, el aislamiento social y la privación materna generan un alto nivel de estrés que compromete la inmunidad y favorece enfermedades gastrointestinales (Rhouma et al. 2017, Kim et al. 2022).
Además de factores externos, la DPD suele asociarse a Escherichia coli enterotoxigénica (ETEC; en español también citada como ECET), bacteria con gran capacidad de adherirse al epitelio intestinal mediante fimbrias, principalmente F4 y F18. Una vez adherida, produce enterotoxinas termolábiles (LT) o termoestables (STa y STb), que interfieren en la absorción de agua y sales y provocan diarrea acuosa severa (Kim et al. 2022). El diagnóstico de ETEC porcina se basa en la detección conjunta de al menos un gen de toxina (eltA, estI, estII) y un gen fimbrial (F4, F5, F6, F18, F41) en un mismo aislado (Vereecke et al. 2023).
Recientemente, se ha descrito un subgrupo emergente de E. coli que no porta genes fimbriales clásicos, pero es positivo para aidA , el gen que codifica la adhesina autotransportadora AIDA-I. Aunque estas cepas carecen de los factores de adhesión típicos de ETEC porcina, se ha demostrado que pueden inducir una colonización intestinal severa y formar biopelículas, contribuyendo al desarrollo de diarrea (Kim et al. 2022). Asimismo, se han identificado cepas portadoras del gen astA, que codifica la toxina termoestable enteroagregativa EAST-1, detectada en aislados porcinos con DPD, aunque su papel patogénico aún se considera controvertido (Vereecke et al. 2023).
La prevención de la infección por ETEC en el período posdestete es fundamental para preservar el crecimiento y el bienestar de los cerdos. Una práctica común es la incorporación de antimicrobianos (AM) en el alimento, junto a coadyuvantes que contribuyen a reducir la incidencia de enfermedades. Aunque los AM siguen siendo clave en la prevención y control de la colibacilosis, su uso irracional ha favorecido la emergencia y diseminación de bacterias resistentes (Kim et al. 2022, Li et al. 2024).
La creciente resistencia a los antimicrobianos (RAM) compromete la eficacia de los tratamientos frente a infecciones bacterianas como la producida por ETEC y otras enfermedades relevantes en producción animal. Las bacterias poseen una notable capacidad de adaptación, favorecida por su rápida replicación, plasticidad genética y la transferencia horizontal de genes. La presión selectiva ejercida por el uso excesivo o inadecuado de AM favorece la diseminación de cepas resistentes en los animales y en su entorno (Kim et al. 2022, Li et al. 2024). Esta situación no solo compromete la salud y el bienestar animal, sino que también constituye una amenaza para la salud pública por la posible transmisión de bacterias resistentes o sus genes a los seres humanos a través de la cadena alimentaria o el ambiente. Frente a esta problemática, la Organización Mundial de la Salud (OMS) promueve un abordaje integral bajo el enfoque de “Una Salud”, que reconoce la interconexión entre la salud humana, animal y ambiental, e impulsa estrategias coordinadas para reducir el uso inadecuado de AM y frenar el avance de la RAM (Gómez et al. 2022, WHO 2022). En este contexto, el objetivo de este trabajo fue aislar cepas de E. coli a partir de muestras fecales de lechones con DPD en granjas de la provincia de Córdoba, Argentina, describir su perfil de resistencia a antimicrobianos de importancia crítica en salud pública y/o animal, y realizar su caracterización genotípica.
Muestreo y aislamiento. Se realizó un muestreo dirigido sobre lechones en el período posdestete (21 a 40 días de edad) con signos clínicos de diarrea, procedentes de 12 lotes pertenecientes a seis establecimientos de producción intensiva ubicados en las localidades de Despeñaderos, Lozada, Montecristo y Monte Maíz, en la provincia de Córdoba. Cada lote presentaba un número variable de lechones (entre 46 y 320), con una proporción de individuos con diarrea que osciló entre el 3% y el 31%. En función de esta variabilidad, el tamaño de la muestra se determinó de acuerdo con el número de animales afectados presentes al momento del muestreo: cuando los casos fueron pocos se incluyeron todos, y cuando fueron numerosos se seleccionó una fracción representativa. En total se obtuvieron 69 muestras de materia fecal. El procedimiento fue aprobado por el Comité Institucional para el Cuidado y Uso de Animales de Laboratorio (CICUAL) de la Universidad Católica de Córdoba (protocolo N° 014).
Algunos de los animales incluidos en el estudio habían recibido tratamiento AM previo a la toma de muestras. Para incorporar esta variable al análisis, se consultó al veterinario responsable de cada granja antes del muestreo, registrando si los animales habían recibido AM y, en tal caso, el tipo administrado. Esta información fue considerada en el análisis posterior de los resultados de los aislamientos bacterianos y perfiles de RAM.
Cada muestra se obtuvo del contenido rectal con hisopo estéril, transportada en medio Stuart a 4 °C y procesada dentro de las 24 h. El procedimiento de aislamiento bacteriano se centró exclusivamente en E. coli, agente principal de la DPD y organismo centinela en la vigilancia de RAM, por lo que no se intentó recuperar otros patógenos entéricos (EFSA 2024). Las muestras se sembraron en agar EMB (eosina-azul de metileno, Britania®, Argentina) e incubaron a 37 °C durante 24 h; de cada cultivo se seleccionó una colonia con brillo verde metálico, presuntamente E. coli, la cual fue caracterizada mediante pruebas bioquímicas convencionales (Koneman et al. 1999) y, tras su confirmación, crioconservada a −80 °C.
En los casos en que no se observaron colonias con morfología típica en EMB o cuando las pruebas bioquímicas resultaron negativas, el procedimiento se repitió a partir del mismo hisopo, previamente colocado en agua de peptona tamponada y conservado a 4 °C. Se realizaron un máximo de tres resiembras consecutivas por muestra; en ausencia de crecimiento típico o confirmación positiva de E. coli, la muestra fue clasificada como negativa.
Evaluación de resistencia. Se evaluó la susceptibilidad de cada cepa frente a ocho AM de importancia crítica para la salud pública y/o animal (OMS 2024, OMSA 2024), mediante la prueba de microdilución en caldo. Esta metodología permitió determinar las concentraciones mínimas inhibitorias (MIC) y, consecuentemente, las proporciones de cepas sensibles, intermedias o resistentes. La clasificación se realizó de acuerdo con los puntos de corte clínicos según CLSI (2023), la cual también fue considerada para la ejecución del ensayo. Como control se empleó E. coli ATCC 25922. Los AM ensayados fueron amoxicilina (AMX), ceftiofur (CFT), enrofloxacina (ENR), estreptomicina (EST), florfenicol (FFC), gentamicina (GEN), oxitetraciclina (TET) y trimetoprim-sulfametoxazol (TMT/SMX), en línea con su relevancia terapéutica en la producción porcina y su representatividad de distintas clases de AM de importancia crítica para la salud pública y animal.
Por otra parte, se cuantificaron las cepas multirresistentes (MDR), definidas como aquellas no susceptibles a al menos un agente AM en tres o más clases (Magiorakos et al. 2012). De los 8 AM ensayados frente a E. coli, se consideraron siete clases AM: penicilinas (AMX), cefalosporinas de 3ª generación (CFT), fluoroquinolonas (ENR), fenicoles (FFC), tetraciclinas (TET), aminoglucósidos (GEN y EST, considerados como una sola clase), y sulfonamidas/diaminopirimidinas (TMT/SMX).
Caracterización genotípica. La determinación genotípica de E. coli enterotoxigénica (ETEC) fue realizada mediante PCR con el fin de identificar genes específicos relacionados con la adhesión y la producción de toxinas. Se empleó E. coli ATCC 25922 como control negativo y la cepa de referencia E. coli H10407 como control positivo. Adicionalmente, se utilizaron aislamientos propios previamente caracterizados como controles positivos para determinados genes. Se analizaron los genes de adhesión fimbrial faeG (F4), fanC (F5), fasA (F6) y fedA (F18), así como el gen no fimbrial aidA (AIDA-I). Además, se incluyeron los genes estI, estII, eltA y astA, que codifican las toxinas STa, STb, LT y EAST-I, respectivamente. Los genes analizados y secuencias de oligonucleótidos cebadores utilizados para la caracterización de los aislamientos ETEC se basaron íntegramente en el protocolo descrito por Moredo et al. (2012). Se consideraron ETEC aquellos aislamientos de E. coli que presentaron al menos uno de los genes estI, estII o eltA, responsables de la codificación de las toxinas STa, STb o LT, respectivamente. Los aislamientos que no cumplieron con este criterio fueron clasificados como no ETEC.
Para la extracción de ADN, cada cepa aislada fue suspendida en un buffer Tris-EDTA/Tritón (TE), sometida a lisis en un baño seco a 100 °C durante 10 minutos, y luego centrifugada a 1.500g durante 15 minutos a 4 °C para obtener el sobrenadante de cada muestra. La concentración y pureza del ADN se evaluaron mediante NanoDrop™, utilizando 1 µL de cada muestra para medir su absorbancia.
La PCR se realizó mediante la preparación de una mezcla compuesta por agua milli-Q, buffer 10x, mezcla de dNTPs, MgCl₂, primers específicos (como EAST-1F, EAST-1R, STa1, Stb1, Sta2, Stb2, entre otros), Taq polimerasa (Macrogen Ligo™), y 5 µL de ADN de la muestra. Las condiciones de amplificación variaron según las recomendaciones del laboratorio Macrogen para cada par de primers, ajustando la temperatura de “annealing” óptimo para cada gen. Las condiciones de amplificación comprendieron desnaturalización inicial a 94 °C durante 5 minutos, seguida de 30 ciclos que incluían desnaturalización a 94 °C por 1 minuto, “annealing” a una temperatura específica para cada par de primers durante 1 minuto, y extensión a 72 °C por 1 minuto. Se realizó una extensión final a 72 °C durante 7 minutos. Posteriormente a la amplificación, las muestras se conservaron a 4 °C y se visualizaron mediante electroforesis en gel de agarosa al 1,5 % durante 35 minutos a 100 voltios. La detección de los productos de PCR se llevó a cabo utilizando un transiluminador a una longitud de onda de 302 nanómetros.
Análisis estadísticos. Las asociaciones entre las variables de interés se evaluaron mediante odds ratios (OR) con sus intervalos de confianza del 95% (IC95%), aplicando el test exacto de Fisher con un nivel de significancia de p<0,05. Primero, se analizó la asociación entre la exposición previa a tratamientos AM y la resistencia de E. coli, tanto en forma global (considerando resistencia a cualquiera de los ocho AM evaluados) como individualmente para cada uno. Luego, se examinó la relación entre el antecedente de tratamiento AM previo y la probabilidad de aislamiento de cepas ETEC. Finalmente, se evaluó la probabilidad de que las cepas clasificadas como ETEC presentaran resistencia a uno o más AM en comparación con las cepas no ETEC. Todos los cálculos se efectuaron con el software Epi Info™ v. 7.2.7 (CDC 2025).
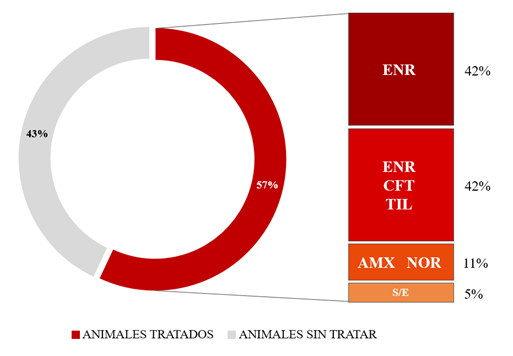
Se observó una prevalencia del 97% de E. coli en las 69 muestras de hisopado rectal analizadas. Solo dos muestras resultaron negativas para el agente en estudio, correspondientes a un cerdo previamente tratado con enrofloxacina y a otro sin tratamiento previo. De acuerdo con los registros veterinarios por establecimiento, 37 animales de los muestreados habían recibido tratamiento previo con AM. Entre los más utilizados, 15 animales recibieron enrofloxacina, otros 16 fueron tratados con una combinación de enrofloxacina, ceftiofur o tilosina, sin posibilidad de determinar cuál de estos fue administrado a cada individuo. Dos animales recibieron amoxicilina o norfloxacina, y en cuatro casos no se obtuvo información sobre el AM administrado. Treinta animales (43%) no habían recibido tratamiento AM previo (Figura 1).
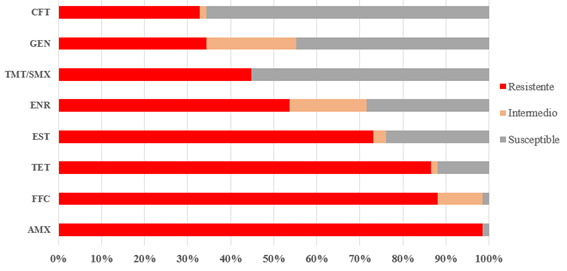
El 97% de las cepas aisladas presentó resistencia a uno o más AM. Como se muestra en la Figura 2, las proporciones de cepas resistentes variaron entre 32,8% y 98,5%, observándose los valores más altos frente a AMX (98,5%), FFC (88,0%) y TET (86,6%). Le siguieron EST (73,1%), ENR (53,7%), TMT/SMX (44,8%), GEN (34,3%) y CFT (32,8%).
A su vez, el 92,5% de las cepas se clasificó como MDR cuando presentó resistencia a tres o más clases AM. Todas las cepas MDR mostraron resistencia a AMX y FFC, y al menos la mitad también lo fue frente a otros AM, incluyendo ENR, TET y GEN. Si bien la mayoría de las cepas fue resistente a tres o cuatro clases, un 7,5% mostró un perfil multirresistente más amplio, con falta de susceptibilidad frente a siete clases (Tabla 1).

* Se consideró multirresistencia la falta de susceptibilidad a tres o más clases AM.
El análisis estratificado global no evidenció una asociación estadísticamente significativa entre la exposición previa a tratamientos AM y la resistencia de E. coli a los ocho AM evaluados (OR 0,83; IC 95 %: 0,58-1,19; p>0,05; n = 67). A su vez, el análisis individual por AM tampoco mostró asociaciones significativas (Tabla 2).
Por otra parte, de los 67 aislamientos realizados en cerdos con DPD, 47 (70%) fueron clasificados como ETEC al presentar al menos uno de los genes responsables de la codificación de las toxinas estI, estII o eltA. De estos, 44 (93,6%) fueron positivos para los genes estI (STa, 63,8%) y estII (STb, 74,5%), observándose esta combinación en cinco de las seis granjas estudiadas (Tabla 3). Asimismo, el 17% de los aislamientos resultó positivo para eltA (LT) detectándose en tres de las seis granjas evaluadas. De estos aislamientos, el 62% presentó LT en combinación con STa, mientras que el 12,5% lo hizo únicamente junto a STb. Entre los genes que codifican la expresión de adhesinas, el más frecuente fue fedA (F18, 21,3%), seguido por faeG (F4, 14,9%). Todos los aislamientos estudiados fueron negativos para fanC (F5) y fasA (F6). En este estudio, se identificó el gen aidA responsable de la adhesina AIDA-I en 12 de los 47 aislamientos clasificados como ETEC (25,5%), en combinación con STa/STb/EAST-I/LT/F4. Respecto al gen astA (EAST-I), se observó la presencia del gen correspondiente en un 14,9% de las cepas ETEC, combinándose en un 25% de los casos con STa, un 17,8% con STb, y en un 10,7% con AIDA-I.
Entre los genotipos más complejos se identificaron combinaciones como estI, estII, astA, faeG y aidA (n = 2), así como estI, estII, eltA, astA y faeG (n=1), ambos pertenecientes a una misma granja ubicada en Montecristo.
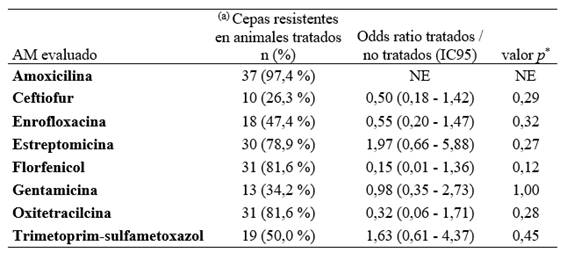
a) Total de animales tratados = 37; Total de cepas analizadas = 67; IC95: intervalo de confianza del 95 %; NE: no estimable; en celdas con valor 0 no fue posible calcular el IC95. Ninguna comparación alcanzó significancia estadística (p<0,05).
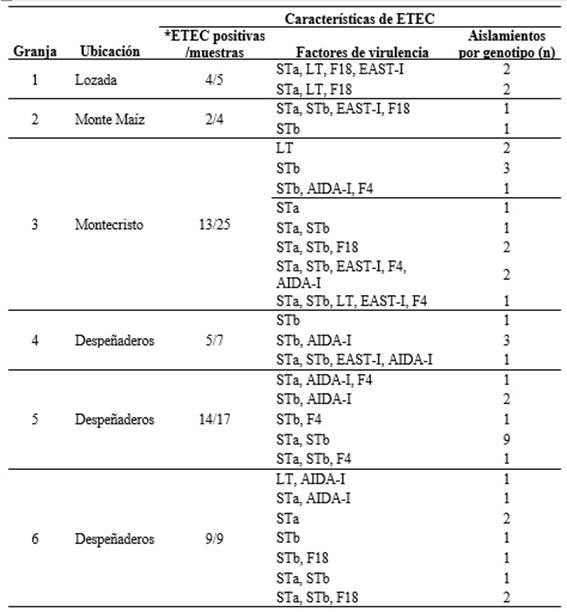
STa: toxina termoestable tipo a; STb: toxina termoestable tipo b; LT: toxina termolábil; F4 y F18: fimbrias; AIDA-I: adhesina involucrada en la adherencia difusa; EAST-I: toxina termoestable tipo 1; *ETEC positivas/muestras: número de aislamientos positivos a ETEC en cada granja sobre el total de aislamientos de E. coli obtenidos de muestras fecales en la misma.
Por último, se observó que la probabilidad de aislamiento de ETEC fue entre 1,19 y 2,2 veces mayor en los animales sin tratamiento en comparación con los tratados (p = 0,0023). No se encontraron diferencias significativas entre la clasificación ETEC/no ETEC de las cepas aisladas y la probabilidad de presentar resistencia a uno o más AM.
Según Gómez et al. (2022), en la producción porcina en Argentina, los AM reportados con mayor frecuencia para el tratamiento de infecciones causadas por E. coli y otras bacterias Gram negativas incluyen cefalosporinas de tercera generación, fluoroquinolonas, aminoglucósidos, macrólidos y fosfomicina. En el presente estudio, a partir de la información provista por los veterinarios responsables de cada establecimiento, las fluoroquinolonas, en particular enrofloxacina y norfloxacina, fueron identificadas como los AM más utilizados en las seis granjas evaluadas. En segundo lugar, se destacaron la tilosina y el ceftiofur como los AM de uso frecuente. La administración de estos fármacos fue principalmente por vía parenteral, en el marco de estrategias metafilácticas. Es importante destacar que el 47% de los cerdos no recibió tratamiento AM, lo cual representa un aspecto positivo en términos de reducción del uso de AM. No obstante, los AM empleados corresponden a categorías de alta relevancia. Según la OMSA (2024) son considerados de importancia crítica, mientras que la OMS (2024) ubica a los macrólidos en esa categoría y clasifica a las fluoroquinolonas y a las cefalosporinas de tercera generación como AM de importancia crítica de máxima prioridad, debido a su papel esencial en el tratamiento de infecciones graves.
E. coli es considerado a nivel internacional como organismo centinela en los programas de vigilancia de la RAM, debido a su carácter comensal, su amplia distribución y su utilidad como indicador de la presión selectiva ejercida por el uso de AM en animales de producción (EFSA 2024). En función de este rol, se evaluó la resistencia en cepas de E. coli aisladas de lechones en producción intensiva, con resultados de MDR que coinciden con los reportados en estudios previos en cerdos de sistemas intensivos. A nivel regional, Gómez et al. (2022) reportaron un 97,3% de cepas resistentes aisladas de ambientes como el piso de corrales de cerdos de distintas categorías en las provincias de Buenos Aires, Santa Fe, Entre Ríos y San Luis, cifra que coincide con el 97% de cepas resistentes a uno o más AM detectado en este estudio. Además, el 49,3% de las cepas en su ensayo fueron resistentes a 6-7 clases AM, resultado que guarda concordancia con los valores observados en esta investigación. De manera similar, Moredo et al. (2015) habían documentado previamente altos niveles de resistencia (95% a más de un AM) en la provincia de Buenos Aires, lo que respalda la persistencia de esta problemática en la región.
Las clases de AM con mayores índices de resistencia en nuestro estudio fueron las penicilinas, los fenicoles y las tetraciclinas. En particular, la resistencia a penicilinas alcanzó el 98,5%, un valor cercano al 100% previamente informado por Faccone et al. (2019), quienes destacaron a esta clase como una de las más frecuentemente asociadas a cepas resistentes en cerdos con diarrea. En contraste, estudios realizados en animales sanos reportaron niveles considerablemente menores de resistencia (13,5%) (Moredo et al. 2012). Estos hallazgos permiten inferir que el uso terapéutico frecuente de penicilinas en cerdos con DPD podría actuar como un factor de presión selectiva que favorece la emergencia de cepas resistentes.
Si bien en este estudio el uso previo de AM y la frecuencia de cepas resistentes o multirresistentes no mostró asociaciones significativas, la mayor proporción de resistencia a penicilinas en estos animales concuerda con lo reportado por Burow et al. (2019), quienes sí obtuvieron diferencias significativas en cerdos expuestos a ampicilina. En cambio, para otras clases de AM, distintos estudios han señalado la ausencia de una relación directa entre uso de AM y resistencia, especialmente en períodos de administración de AM limitados (Burow et al. 2019, Bacci et al. 2020).
La elevada resistencia a fenicoles observada en nuestro estudio supera los valores reportados en Argentina por Bessone et al. (2017) en lechones posdestete y confirma la variabilidad regional, con rangos de 47,6% a 82% en diferentes categorías productivas (lactantes, posdestete y adultos) (Bessone et al. 2017, Faccone et al. 2019, Gómez et al. 2022). En el caso de las tetraciclinas, la resistencia se mantuvo elevada y relativamente uniforme en la región durante los últimos años (80-100%), en concordancia con nuestros hallazgos (Moredo et al. 2012, Faccone et al. 2019, Gómez et al. 2022). En contraste, la resistencia a quinolonas y sulfonamidas/diaminopirimidinas fue menor, en línea con lo informado previamente en la región en animales con diarrea. Los aminoglucósidos, en cambio, mostraron valores más altos que los reportados en estudios regionales, donde se observaron rangos de 9,5% a 14% (Bessone et al. 2017, Faccone et al. 2019). Finalmente, la clase con menor frecuencia de resistencia fueron las cefalosporinas de tercera generación, en coincidencia con lo registrado en Argentina por Bessone et al. (2017) en animales con DPD.
La prevalencia de ETEC en este estudio fue del 70%, un valor inferior al reportado por Moredo et al. (2012) y Luppi et al. (2016), quienes identificaron ETEC en el 95% y 94,9% de los aislamientos, respectivamente. Una posible explicación para esta diferencia radica en la exposición previa a tratamientos AM. Aproximadamente la mitad de los animales había recibido AM al momento del muestreo, lo que se asoció con una reducción significativa en la probabilidad de aislar ETEC (p = 0,0023). Es posible que algunos aislamientos de ETEC hayan sido eliminados o inhibidos por el tratamiento, favoreciendo la recuperación de otras E. coli de la microbiota intestinal. De este modo, el uso previo de AM podría haber alterado la composición bacteriana al momento del muestreo y limitado la detección del verdadero agente etiológico de la colibacilosis.
Debe considerarse, además, que en este estudio se intentó exclusivamente el aislamiento de E. coli, aunque otros patógenos también pueden causar DPD. Asimismo, se seleccionó un único aislado representativo por muestra, procedimiento habitual en estudios epidemiológicos de DPD (Luppi et al. 2016, Vereecke et al. 2023), que reduce duplicaciones, pero no descarta la presencia de otros clones de E. coli en las mismas muestras.
La enterotoxina más prevalente fue STb, detectada en el 74,5% de los aislados, la cual se asocia comúnmente con una grave pérdida de líquidos en el intestino delgado de los lechones destetados. La mayor frecuencia de STb en comparación con STa concuerda con los informes de Luppi et al. (2016). Además, el 44,7% de las cepas analizadas presentaron la combinación de genes estI (STa) y estII (STb), un valor superior al 16% informado por Moredo et al. (2012) para esta misma combinación.
En cuanto a la distribución de toxinas, se ha descrito previamente la existencia de cepas que poseen únicamente toxinas sin adhesinas conocidas y viceversa, lo que sugiere que otros factores de virulencia no evaluados podrían desempeñar un papel en la patogénesis de la DPD (Luppi et al. 2016). En este estudio no se evaluó la presencia de los genes paa y f41, asociados a la adherencia en cerdos, ni del gen eae, característico de cepas enteropatógenas (EPEC) y enterohemorrágicas (EHEC). Por lo tanto, no puede descartarse la presencia de estos patotipos entre los aislados analizados.
El factor de adhesión fimbrial más frecuente fue F18, en concordancia con otras investigaciones (Moredo et al. 2012, Bessone et al. 2017). Esta elevada frecuencia era esperable, dado que F18 está ampliamente asociado con cepas de E. coli responsables de DPD. En contraste, la colibacilosis neonatal suele estar vinculada a cepas que expresan F4, con una menor participación de F5, F6 y F41.
Además de las fimbrias, se analizaron adhesinas no fimbriales, entre las cuales el gen aidA fue detectado en el 25,5% de los aislamientos. Este gen, implicado en la adherencia a las células epiteliales del intestino, ha sido vinculado con la capacidad de ciertas cepas para persistir y diseminarse en el hospedador. Los genotipos más complejos del estudio incluyeron la presencia del gen aidA en combinación con varios factores de virulencia, como STa, STb, EAST-I y F4, detectados en dos aislamientos procedentes de una misma granja ubicada en Montecristo. Estas cepas presentaron un perfil de resistencia bacteriana intermedio, con resistencia a cuatro o cinco AM, incluyendo AMX, EST, FFC, TET y TMT/SMX. La presencia del gen aidA en estas cepas representa un hallazgo relevante desde el punto de vista de la salud pública, dado su papel potencial en la transmisión entre animales y humanos (Zhao et al. 2009, Do et al. 2020).
Otro factor de virulencia identificado en este estudio fue la toxina EAST-I, detectada en el 14,9% de los aislamientos. Esta toxina se encontró en combinación con STa en el 25% de los casos, con STb en el 17,9%, y con AIDA-I en el 10,7%. La coocurrencia de EAST-I con enterotoxinas como STa y STb podría sugerir un efecto sinérgico en la patogénesis de la DPD, al potenciar la secreción intestinal de líquidos y prolongar la duración del cuadro clínico. Aunque su presencia conjunta con AIDA-I fue menos frecuente, esta asociación también resulta de interés, ya que la adhesina AIDA-I puede favorecer una colonización más eficiente del epitelio intestinal, lo que podría contribuir a una mayor severidad de la infección (Fairbrother et al. 2005, Do et al. 2020).
Los genotipos identificados en este estudio muestran similitudes con los reportados en otras investigaciones realizadas en la provincia de Córdoba, Argentina (Moredo et al. 2012, 2015). Esta concordancia sugiere la posible circulación de ciertos perfiles genéticos de E. coli en la región. No obstante, la variabilidad observada en la distribución de factores de virulencia entre estudios podría deberse a múltiples factores, como la ubicación geográfica, la categoría productiva o el estado sanitario de los animales (Tabla 4). Estos resultados refuerzan la necesidad de continuar monitoreando las poblaciones bacterianas locales, considerando las particularidades de cada sistema de producción, para comprender mejor la dinámica de estos agentes y su potencial impacto en la salud animal y pública.
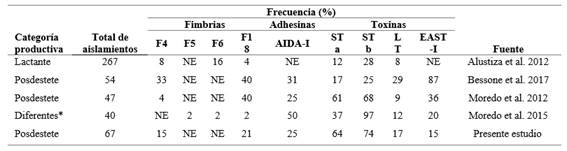
STa: toxina termoestable tipo a; STb: toxina termoestable tipo b; LT: toxina termolábil; F4, F5, F6, F18: fimbrias; AIDA-I: adhesina involucrada en la adherencia difusa; EAST-I: toxina termoestable tipo 1; NE: no estudiada; *Diferentes: incluye categoría lactante, posdestete y terminación.
Los resultados de este estudio muestran que una elevada proporción de cerdos con DPD en granjas de la principal región productiva de Córdoba portan ETEC con perfiles de MDR frente a AM de uso habitual tanto en medicina veterinaria como humana. La alta frecuencia de RAM observada podría estar asociada a la presión de selección derivada del uso frecuente de estos fármacos y de determinantes ambientales capaces de ejercer co-selección, lo que incrementa el riesgo de diseminación de genes de resistencia en la cadena alimentaria y en el ambiente. En este contexto, resulta fundamental concientizar a los productores y promover, junto con los profesionales veterinarios, el uso racional de antimicrobianos conforme a las recomendaciones de uso prudente. La escasez de datos de referencia sobre la prevalencia de ETEC en la región refuerza la necesidad de continuar generando evidencia local para diseñar estrategias de prevención y control más eficaces en los sistemas de producción porcina.
Agradecimientos. Los autores agradecen a la Universidad Católica de Córdoba, a la Agencia Nacional de Promoción de la Investigación, el Desarrollo Tecnológico y la Innovación, y al Consejo Nacional de Investigaciones Científicas y Técnicas por el apoyo financiero brindado para la concreción del presente trabajo, mediante los proyectos UCC - Convocatoria SIV 2022, PICT 2019-2019-002495 y PUE N° 22920180100034CO, respectivamente.
Contribución de los autores. La conceptualización y el diseño metodológico del estudio fueron realizados por L-NJ, L-AM. La investigación, que comprendió el trabajo de campo y la recolección de muestras, fue realizada por L-AM y H-MA. El aislamiento y la caracterización bacteriológica de las cepas obtenidas fueron efectuados por Z-MP, H-MA y Z-AP. Las pruebas de susceptibilidad antimicrobiana, incluyendo los ensayos de microdilución y la determinación de concentraciones inhibitorias mínimas, fueron llevadas a cabo por Z-MP, V-JP y Z-AP. Finalmente, el análisis genotípico de los aislamientos fue realizado por V-JP y Z-MP. La validación de los datos y la supervisión del trabajo analítico fueron realizadas por L-NJ. El análisis formal y la interpretación de los resultados estuvieron a cargo de Z-MP y L-NJ. La redacción del borrador original fue realizada por Z-MP, y la revisión y edición del manuscrito por L-NJ, con la colaboración de todos los autores. La adquisición de financiamiento y la administración del proyecto estuvieron a cargo de L-NJ, V-JP y L-AM.
Declaración de conflictos de intereses. Los autores declaran que no existe ningún conflicto de intereses financiero, personal o académico que pueda haber influido de manera inapropiada en la realización de este estudio o en la interpretación de sus resultados.
Disponibilidad de datos. Los datos estarán disponibles previa solicitud.